荔园非编码RNA平台——miRNA靶点筛选
实验原理
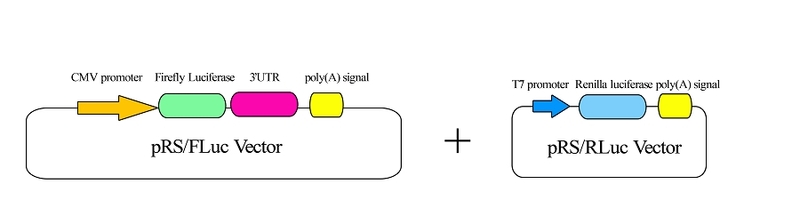
miRNA通过碱基配对结合到靶mRNA的3’UTR区,抑制靶基因的翻译或对靶基因mRNA的降解达到调控基因表达的目的。将靶mRNA的3’UTR区构建至萤火虫荧光素酶报告基因的3’端,与miRNA表达载体及海肾荧光素酶报告基因载体共转染细胞,先后加入两种底物荧光素,通过对荧光素酶报告基因的表达检测确认miRNA对靶基因的调控效果。下图为双荧光素酶报告基因检测载体的示意图。
![]()
技术应用
通过miRNA靶标的鉴定从而进行miRNA功能的深入研究。
实验流程
![]()
![]()
实验结果实例
![]()
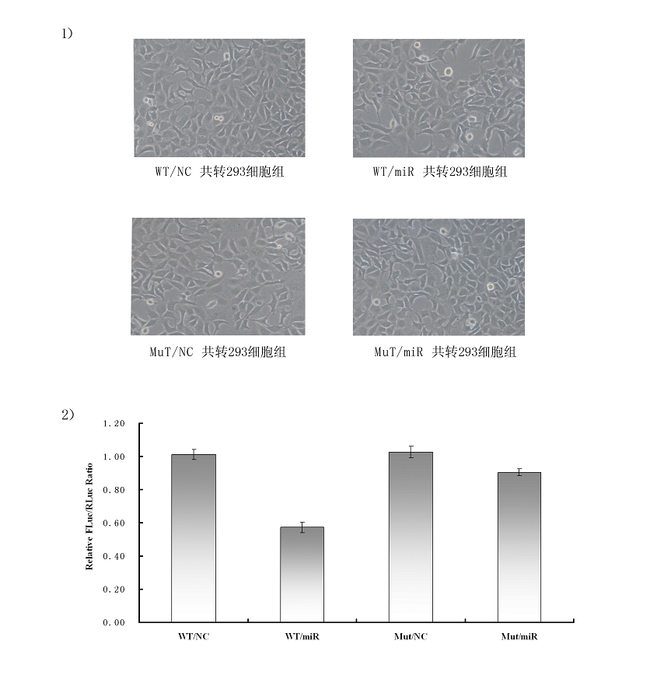
图 1 hsa-miR-9-1 的靶点筛选结果
1)四组质粒的 293 细胞共转染后的细胞照片;2)四组细胞的双荧光素酶报告基因检测柱形图。
注:WT为野生型3'UTR 区的萤火虫荧光素酶报告基因质粒,Mut为突变型3'UTR 区的萤火虫荧光素酶报
告基因质粒,结果表明待研究的 miRNA 对靶基因有较明显的调控作用。
TROUBLESHOOTING
|
实验问题
|
原因
|
推荐解决方法
|
|
发光检测值过低?
|
荧光素酶表达多低
|
注意调整细胞状态、转染条件、转染量,提高发光值。
|
|
检测试剂
|
避免反复冻融以及保存时间过长。
|
|
发光检测值过高?
|
荧光素酶表达过高
|
建议通过降低转染量或减少检测体积等降低发光。
|
常见问题FAQ
Q :有哪些数据库可对miRNA的靶基因进行预测分析?
A :根据miRNA 5‘ 端2-8个核苷酸可与靶mRNA 3‘ UTR区完全互补这一特点,结合miRNA与靶基因形成二聚体的热力学稳定
|
miRNA靶基因预测方法
|
检测范围
|
算法特点
|
|
miRanda
|
人,果绳,斑马鱼
|
序列匹配,双链结合自由能,物种间保守性
|
|
TargetScan/TargetScanS
|
人,小鼠,大鼠,狗,鸡,蛙,黑猩猩,恒河猴,牛,负鼠
|
提出“miRNA种子区”的概念
|
|
RNAhybrid
|
哺乳动物
|
快速准确计算miRNA-mRNA二聚体自由能
|
|
DIANA-microT
|
人,小鼠,,大鼠,果绳
|
考虑miRNA调控单个靶位
点的情况
|
|
PicTar
|
脊椎动物
|
区分“完全匹配种子区”与“不完全匹配种子区”
|
|
RNA22
|
哺乳动物
|
不考虑保守,由mRNA入手预测相关miRNA
|
Q :荧光素酶报告基因有哪些特点?有哪些应用?
A :在荧光素酶的催化下,荧光素可被氧化并释放光子,可用荧光检测仪对荧光定量测定。荧光素酶检测系统具有非放射性,灵敏度高的特点。荧光素酶咋哺乳动物细胞中的半衰期为3小时,半衰期短不发生积累,故调控元件的改变会即时导致荧光素酶活性的改变,可进行快速方便的分析。我们把感兴趣的基因转录的调控元件克隆在荧光素酶报告基因的上游或下游,构建成报告基因质粒,即可进行启动子、增强子的活性研究,miRNA的靶点筛选工作。
Q :荧光素酶的发光波长是多少?
A :萤火虫荧光素酶催化luciferin发光的最强发光波长为560nm。海肾荧光素酶催化coelenterazine发光的最强发光波长为465nm。
Q :荧光素酶检测系统需要制备标准曲线吗?
A :一般不需作标准曲线。荧光素酶检测系统用于比较样品的相对活性。
Q:双荧光素酶报告基因系统有何优点?
A:在双荧光素酶报告基因测试中,将萤火虫荧光素酶作为实验报告基因,海肾荧光素酶作为对照报告基因。实验报告基因用于测试实验条件下基因的表达,而对照报告基因作为内对照,以使实验报告基因测试的结果归一化。作归一化可消除实验过程中减弱实验准确度的变化,如培养细胞的数量、细胞转染及裂解的效率等。
Q :荧光素酶报告基因与GFP的区别是什么?
|
名称
|
检测方法
|
应用
|
特点
|
|
GFP绿色荧光蛋白
|
显微镜下直接观察
|
转染效率的检测或融合目的蛋白,观察蛋白表达情况
|
方便直观
|
|
荧光素酶报告基因
|
细胞裂解后加入底物在荧光检测仪中进行测定
|
研究启动子的功能与调控
|
可准确定量
|
参考文献
1. Lee DY, Deng Z,Wang CH, et al.MicroRNA-378 promotes cell survival, tumor growth, and angiogenesis by targetingSuFu and Fus-1 expression.PNAS 2007,(104):20350-20355.
2. Dong F, Lou D. MicroR NA-34b/c suppresses uveal melanoma cell proliferation and migration through multipletargets.Molecular Vision 2012,(18):537-546.

 微信扫码
微信扫码
 热线电话
热线电话
 用户中心
用户中心
 意见反馈
意见反馈

 荔园基因
荔园基因

 购物车
购物车